南湖新闻网讯(通讯员 祝桢莹)草莓是经济价值较高的重要水果,在世界范围内广泛种植。草莓不同野生种质和不同栽培品种之间的花序结构存在显著差异。根据花序柄的长短,这些花序可分为基部及顶部分枝等类型。草莓同一花序上第一个果实最大,高级次果实逐渐变小,且不同分枝类型对各级果实大小均一性影响显著,是较为独特的发育现象。然而,草莓不同花序分枝类型形成的遗传学基础仍不清楚。

近日,The Plant Cell期刊在线发表了华中农业大学果蔬园艺作物种质创新与利用全国重点实验室/湖北洪山实验室康春颖教授团队题为“The Gα protein FveGPA1 regulates inflorescence architecture via the FveBRI1-mediated brassinosteroid pathway in strawberry”的研究论文。该研究在森林草莓中挖掘了调控花序形态建成的两个关键基因,分别编码异三聚体G蛋白α亚基FveGPA1和油菜素内酯(BR)受体FveBRI1,揭示了异三聚体G蛋白与BR信号通路协同调控花序不同节间差异性伸长的分子机理。
研究团队通过EMS诱变在森林草莓中筛选到两个等位突变体basal-branching inflorescence 1-1(bbi1-1)和bbi1-2,呈现出花序柄(peduncle)显著缩短、花柄(pedicel)显著伸长的表型(图1)。遗传分析与基因克隆结果表明候选基因编码异源三聚体G蛋白α亚基FveGPA1,定位于细胞膜。互补实验和CRISPR/Cas9介导的基因编辑实验均证实了这一结果。荧光互补实验表明FveGPA1与Gβ亚基FveAGB1互作,FveAGB1与Gγ亚基FveAGG3互作,说明三者可形成异源三聚体复合物。其中,agg3CR单突变体的花序柄和花柄均缩短,而花轴(rachis)几乎完全缺失。bbi1-1 agg3CR双突变体的花序柄进一步缩短,基部分枝类型花序比例显著高于两个单突变体,表明FveGPA1和FveAGG3协同调控花序形态建成。
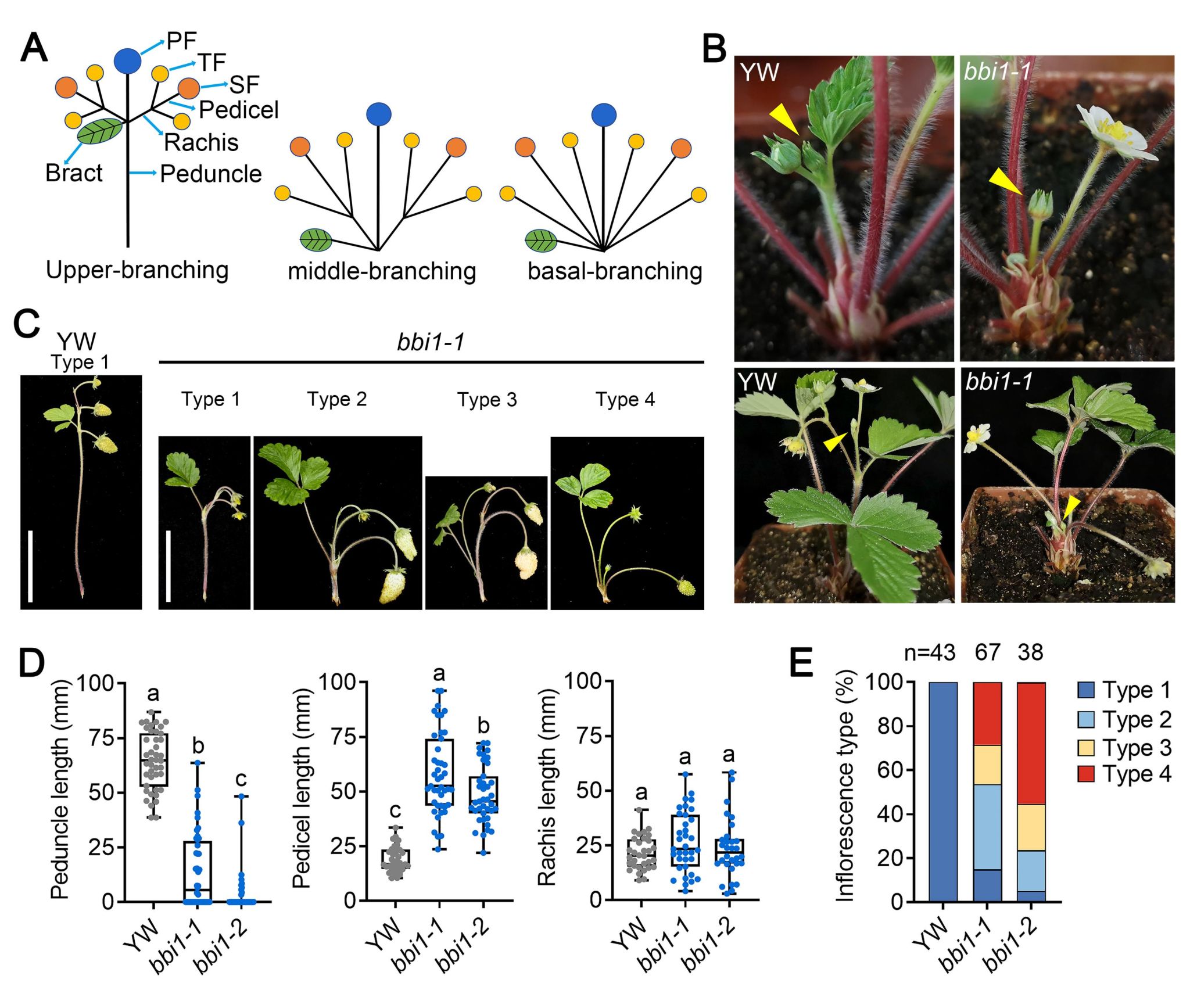
图1 草莓花序结构示意图及bbi1突变体花序表型
另外两个等位突变体bbi2-1和bbi2-2花序表型与bbi1相似,其致突变基因编码BR受体FveBRI1,过表达该基因导致花柄显著缩短,表型与突变体相反。bbi1-1 bbi2-1双突变体的花序完全丧失花序柄和花轴,所有花序均为基部分枝型,表明FveGPA1和FveBRI1存在协同互作。BR处理实验显示,bbi1突变体幼苗的下胚轴和根长均对2,4-表油菜素内酯(eBL)处理的敏感性显著降低;在bbi1突变体中,BR生物合成基因FveCPD和FveBR6OX2及响应基因FveBRH1反馈性上调,且不同BR代谢物含量显著升高(图2)。另外,草莓BR降解酶基因突变体cyp734a129中内源BR含量显著升高,cyp734a129 bbi1双突变体的绝大部分花序为顶部分枝型,即基本挽救了bbi1的基部分枝表型。这些结果证明异三聚体G蛋白通过BR信号通路调控草莓花序形态建成。
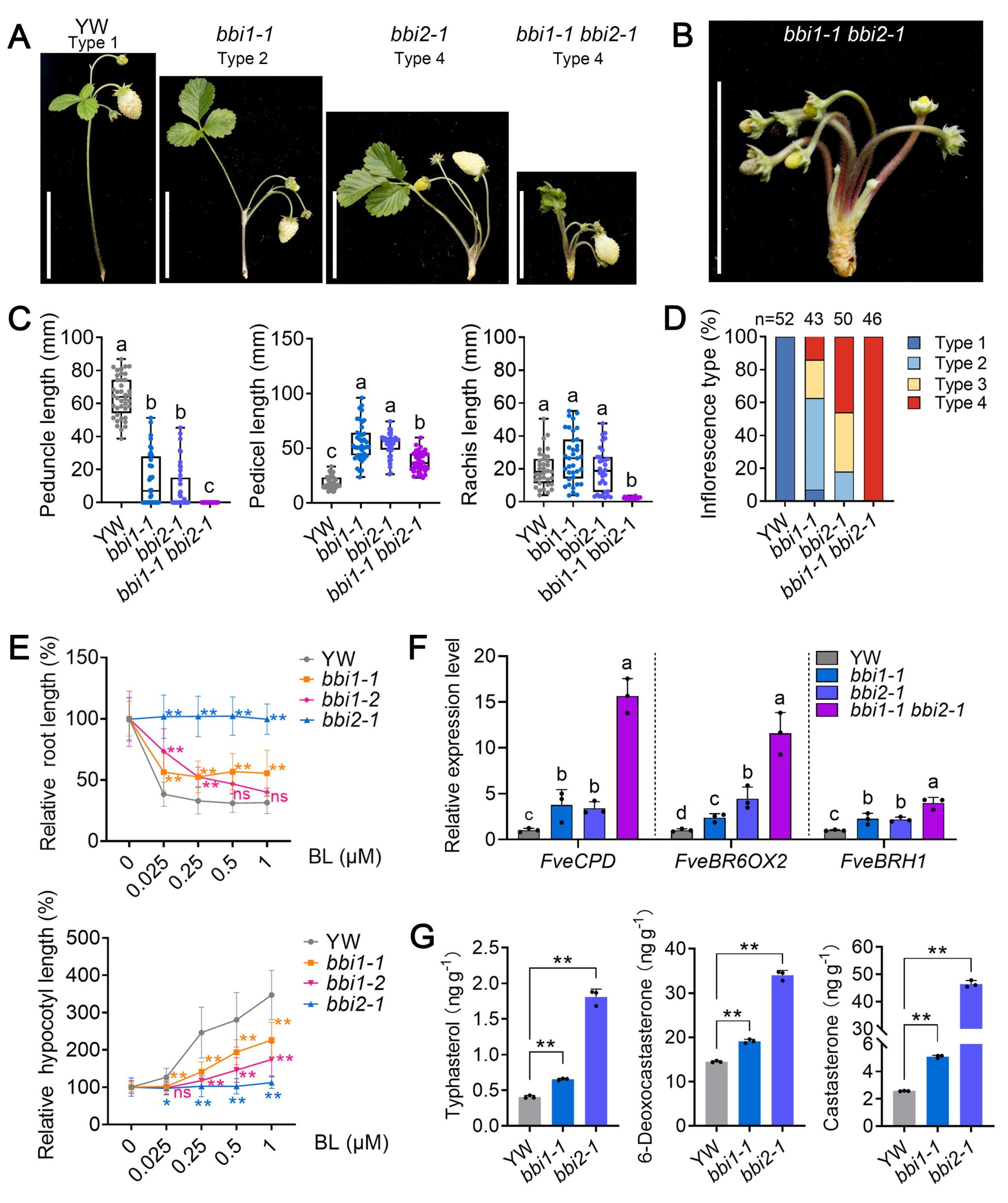
图2 FveGPA1通过FveBRI1介导的BR信号通路调控草莓花序结构
进一步观察发现FveGPA1和FveBRI1在花序发育早期即显著影响了花序柄伸长,在成熟花序中促进花序柄的细胞分裂与扩张,却抑制了花柄的细胞分裂与扩张,呈现组织特异性调控。对野生型及两种突变体花序柄和花柄进行转录组分析,发现bbi1和bbi2花柄中52%差异表达基因相同,BR生物合成通路显著富集;细胞周期基因(FveCYCP4;1a、FveCYCP2;1等)和细胞壁扩展蛋白基因(FveEXP1、FveEXP8等)在花序柄和花柄中呈现相反的差异表达模式。在这些差异表达基因中,转录因子FveKNAT6、FvePNY和FveSHI在突变体花序柄中显著上调、在花柄中显著下调,可能是节间伸长的负调控因子。
基于以上结果,研究团队提出草莓花序节间差异伸长的工作模型:FveBRI1介导的BR通路是调控花序节间伸长的主要途径,促进花序柄伸长、抑制花柄伸长;异三聚体G蛋白通过BR受体或下游信号元件汇聚于BR通路;FveGPA1和FveBRI1基因突变可导致花序从顶部分枝型转变为基部分枝型(图3)。该研究首次在草莓中揭示了异三聚体G蛋白与BR通路在花序节间伸长中的组织特异性调控机制,为优化草莓花序结构提供了基因资源和理论依据。
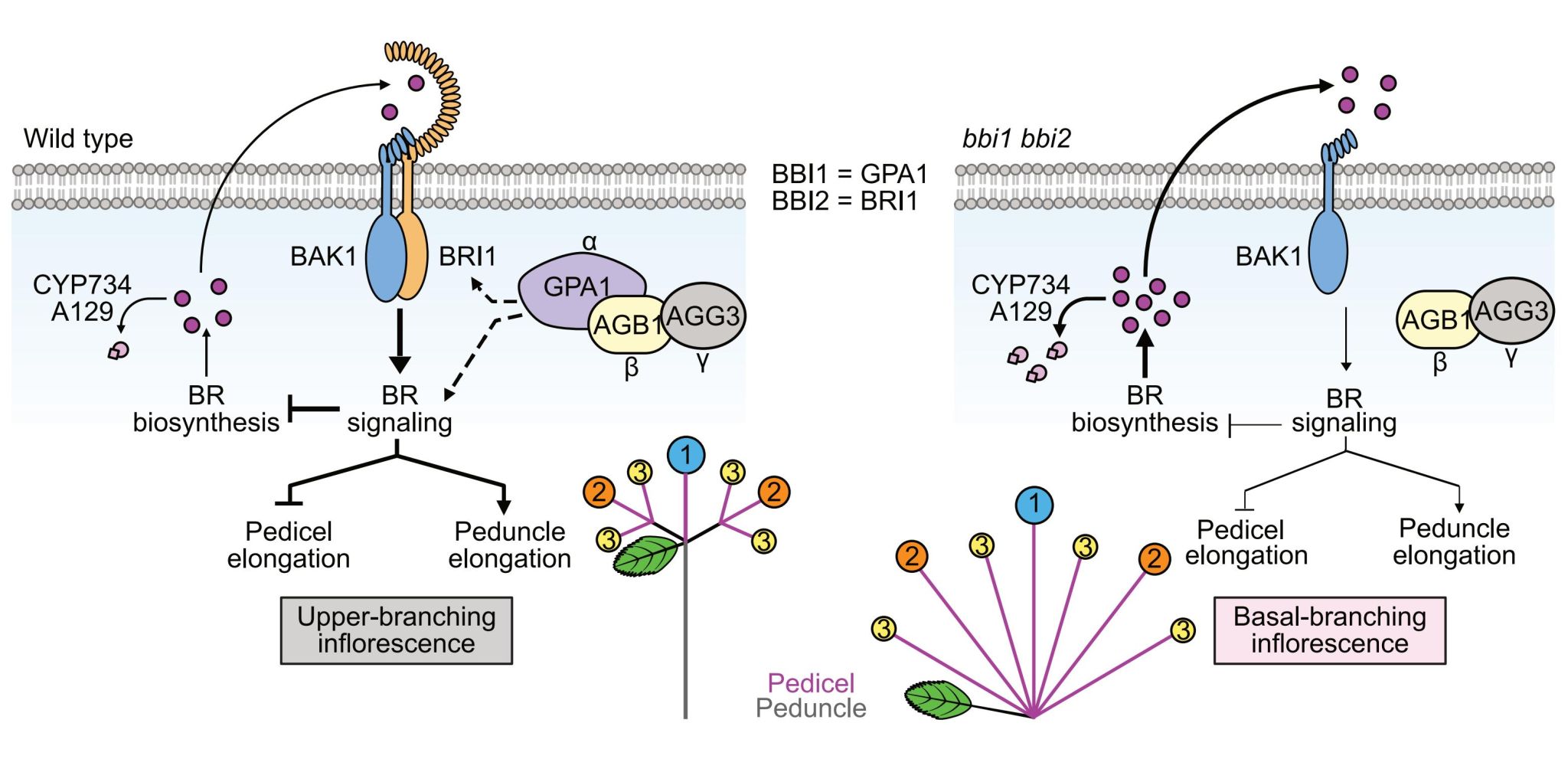
图3 FveGPA1和FveBRI1调控花序结构的工作模型
华中农业大学果蔬园艺作物种质创新与利用全国重点实验室博士研究生祝桢莹为该论文第一作者,康春颖教授为通讯作者。华中师范大学特任副研究员张云明、已毕业博士生韩亚帆、胡少强、安徽农业大学副教授郑光辉、博士生吴娅婷,以及上海交通大学副研究员许鹏博和研究员连红莉等参与了研究工作。该研究得到国家重点研发计划、国家自然科学基金等项目的资助。
审核人:康春颖
论文链接:https://doi.org/10.1093/plcell/koag134